我们很高兴向您介绍Mnova 17——这一里程碑式的版本将尖端技术与清新现代的设计完美融合。该版本进行了重大技术升级,包括迁移至Qt 6,从而确保了更出色的性能、更高的安全性以及面向未来的强大功能。
除了技术上的飞跃,Mnova 17还在Mnova NMR、NMRPredict、MSChrom和Mnova DB等关键插件方面进行了重大改进,并为Mnova Python解释器等工具新增了功能,为用户提供了更强大的分析工作流处理能力。 此外,本次发布还包含Mnova Gears 2.8.0和Chrom Cal 1.2.0等更新版本,并修复了Fraction Analysis 1.1.0和Chrom Reaction Optimization 2.0.1中的错误。
这些改进不仅体现在功能层面:受技术和战略因素的双重驱动,Mnova进行了重大的用户界面重新设计。我们的旗舰产品如今自豪地彰显Mestrelab与SciY的关联,展现出焕然一新的品牌形象。这一转变象征着我们在新的SciY生态系统中对进步、创新与协作的承诺。
焕然一新的Mnova界面
重新设计的用户界面在多个层面进行了改进:
图标和小工具的尺寸已针对更高分辨率进行了优化,呈现出更清晰、更现代的视觉效果。
界面的顶部区域已焕然一新:标题栏的颜色从红色变为鲜艳的洋红色,且“命令面板”始终位于中央,以便更快地进行导航。
深色模式已得到优化,分辨率更高,视觉体验更舒适。
功能区(左上角)中的“文件”选项卡已进行更新,使其与界面其他部分保持一致,从而确保所有选项卡的设计更加统一。
当然,这种全新的界面体验在Windows、Linux和macOS这三个操作系统上保持一致,因此无论使用何种平台,每位用户都能体验到同样现代化的视觉风格和操作体验。
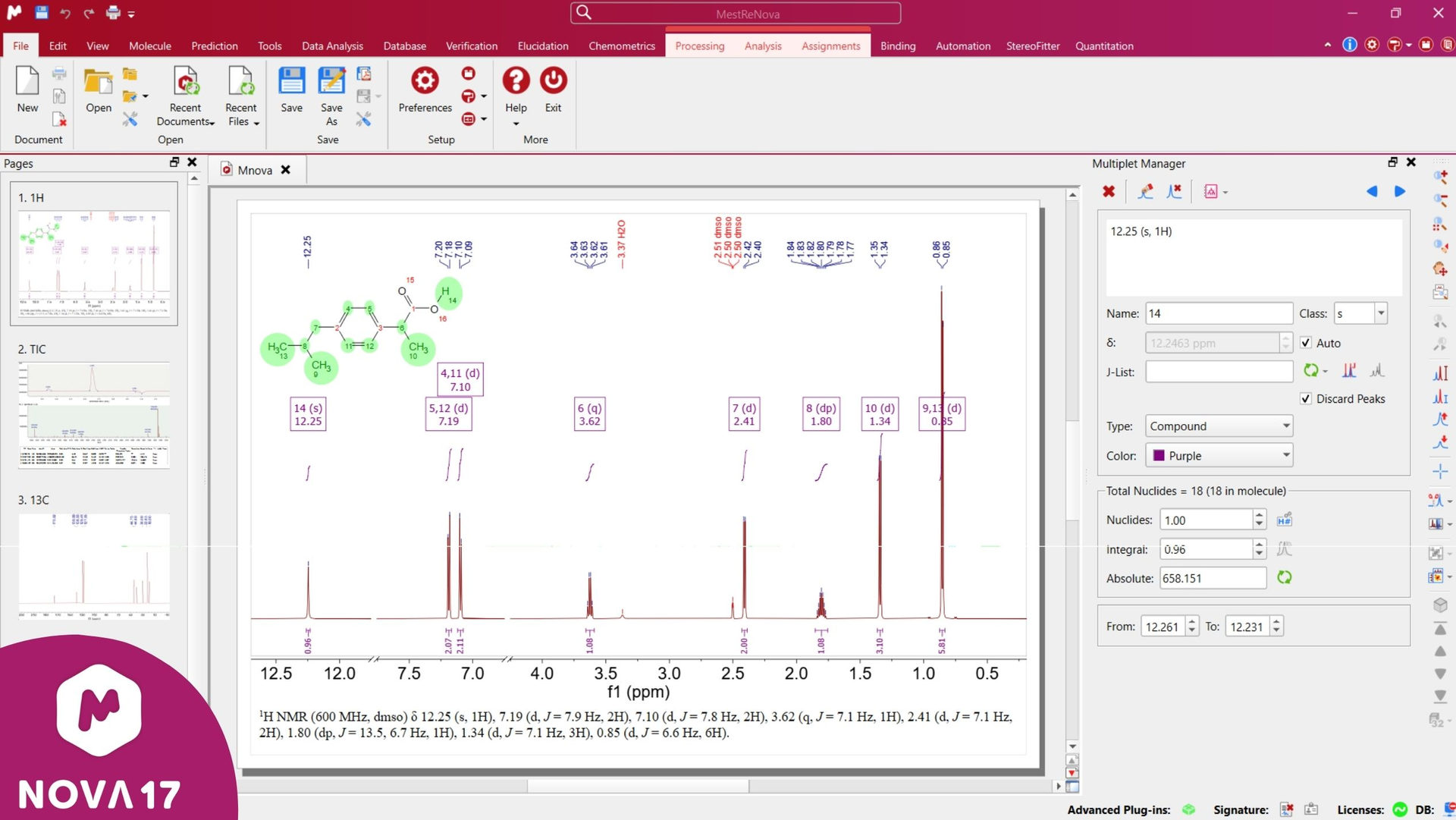 图 1:Mnova 17重新设计的界面截图,重点展示了全新的标题栏、位于中央便于操作的命令面板,以及清晰的高分辨率图标,整体呈现出更简洁、更现代的外观。
图 1:Mnova 17重新设计的界面截图,重点展示了全新的标题栏、位于中央便于操作的命令面板,以及清晰的高分辨率图标,整体呈现出更简洁、更现代的外观。
 图 2:采用深色主题的Mnova 17,展现了更高的分辨率和更细腻的对比度,带来更清晰、更身临其境的视觉体验。
图 2:采用深色主题的Mnova 17,展现了更高的分辨率和更细腻的对比度,带来更清晰、更身临其境的视觉体验。
深入的Python经验
现代科学创新越来越依赖于Python在数据科学、自动化、验证和集成方面丰富的包生态系统。能够在科学分析平台内直接安装和利用Python包,使组织能够扩展核心功能、实现复杂工作流的自动化,并将分析结果与电子实验室笔记本(ELN)、实验室信息管理系统(LIMS)、数据湖以及AI/ML管道等外部系统无缝连接。
为了简化Python包的安装、更新和卸载,Mnova 17引入了一个内置的Python包管理器,可通过功能区中的“工具”选项卡访问:
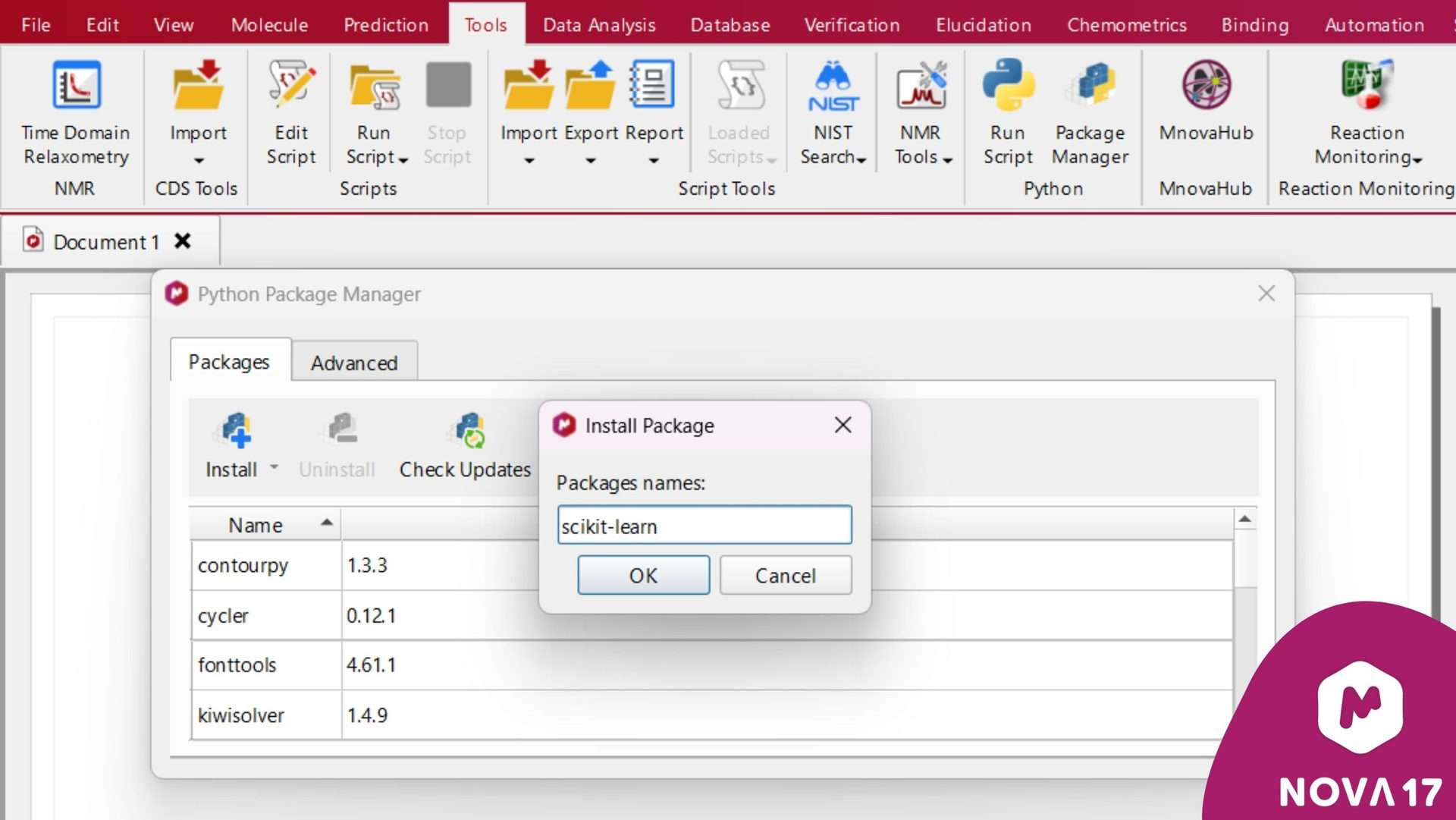
图 3:Python包管理器在安装scikit-learn包时的运行情况。
JSON格式文档的导入/导出
Mnova现已支持JSON格式的NMR、LC/GC-MS数据以及化学结构。借助Mnova 17,用户现在还可以以JSON格式(.mnjs)导出和导入完整的文档,其中包括页面、项目以及原始科学数据。
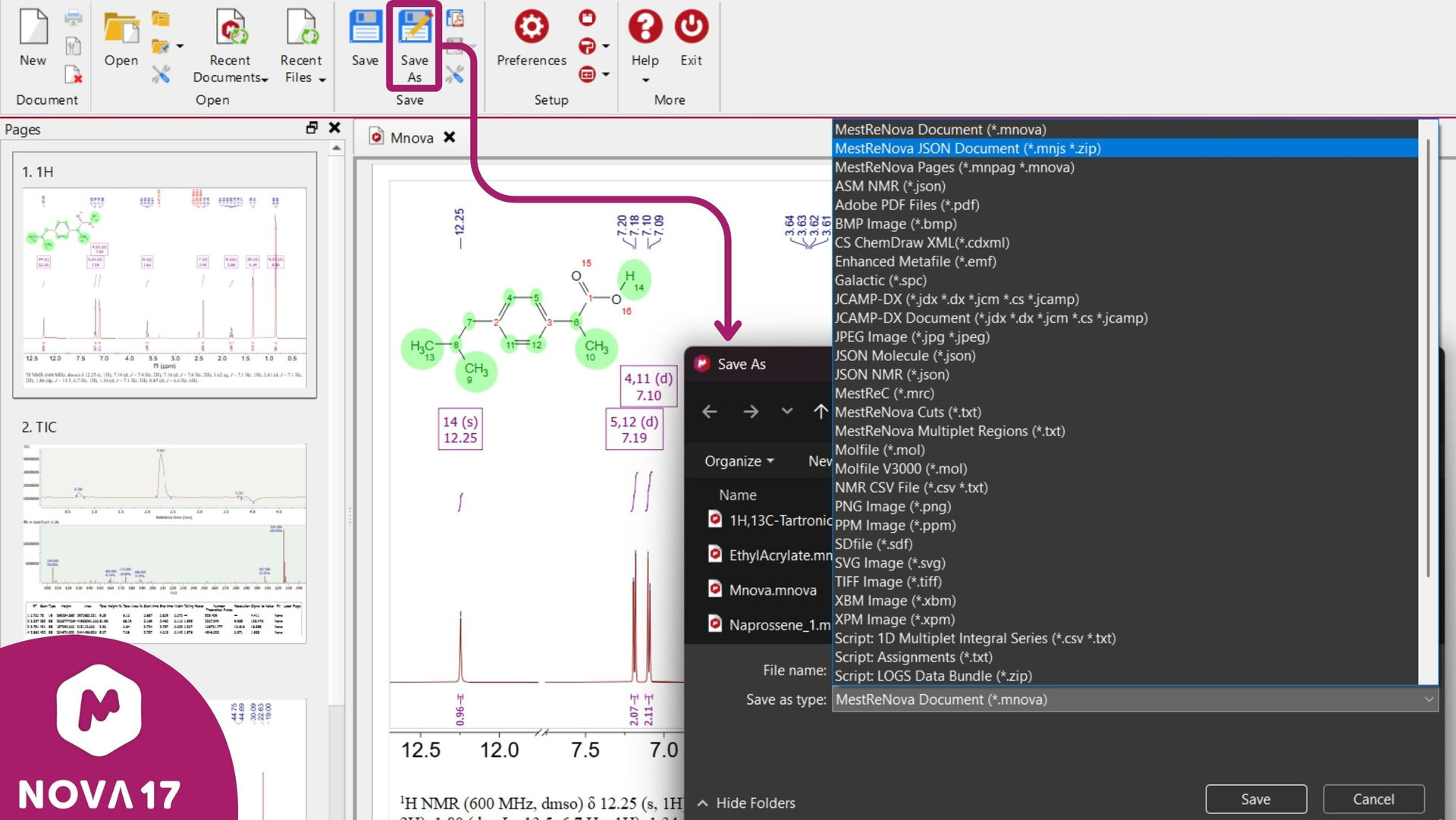
图 4:将Mnova文档保存为JSON格式文档(.mnjs)。
新的.mnjs格式包含:
文档级元数据(版本控制、版式、页面结构)。
包含版式、注释和项目引用的页面定义。
项目级内容存储在模块化JSON文件中,这些文件将原始数据、画布配置和绘图属性分隔开来。
该架构为Mnova内容提供了清晰、可扩展且机器可读的表示形式。其结果是一种对开发者友好的文档格式,既能实现与外部工具的深度集成、可重现的工作流以及高级数据管理,同时又能保持完全的透明度,并方便高级用户和平台集成商进行访问。
基于 GCNN 的新型核磁共振预测模型
Mnova 17推出了一款基于图卷积神经网络(GCNNs*) 的尖端AI预测模型,旨在让NMR谱图预测变得更快、更准确、更可靠。 这些模型经过数万个精心标注的实验波谱训练,能够学习局部分子结构和化学环境如何影响核磁共振化学位移。由此形成了一种基于概率、数据驱动的方法,可提供高度精确的质子和碳位移预测。
这些预测结果为高质量的波谱模拟和自动波谱指派提供了支持,有助于减少结构解析中的不确定性,节省专家时间,并提高在常规和复杂分析工作流程中结构判定结果的可靠性。
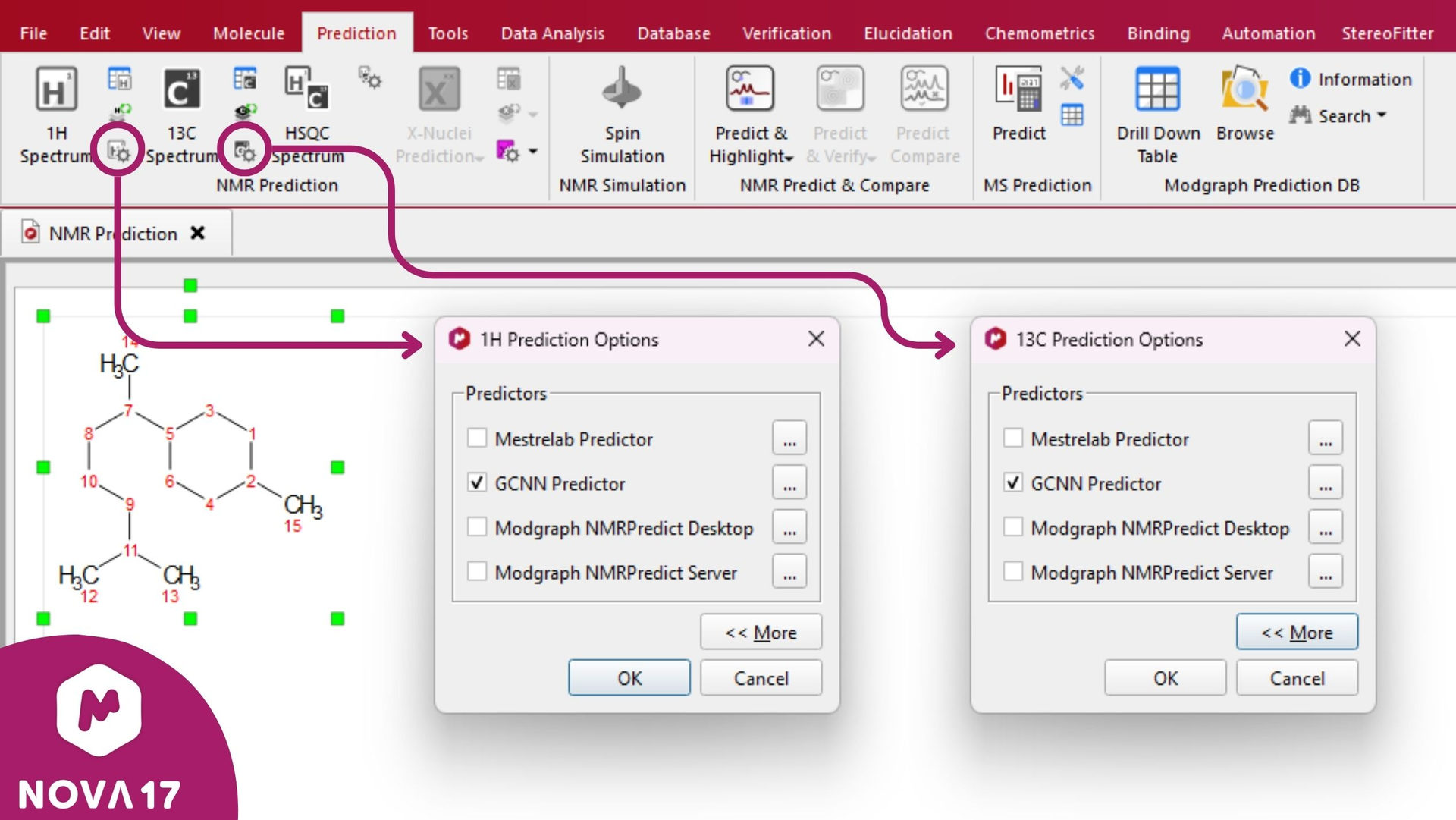
图 5:可通过“预测”功能区中的选项访问 GCNN 预测器。选中后,在根据结构预测波谱时,系统将自动使用 GCNN。
注:GCNN预测器已包含在Mnova NMRPredict插件中,但需激活许可证方可使用。如需申请许可证,请在文章底部扫描二维码联系我们。
*Magn. Reson. 2024, 368, 107795. https://doi.org/10.1016/j.jmr.2024.107795
“动态工具”功能增强
针对多波谱时间序列、T1、T2、T1ρ以及扩散实验的数据分析工作流已进行升级,以提供更清晰的可视化效果、更佳的用户体验以及更强大的功能。分析结果现展示于专用工作区中,便于用户更轻松地进行拟合操作、查看详细信息,并探索数据的内在行为。
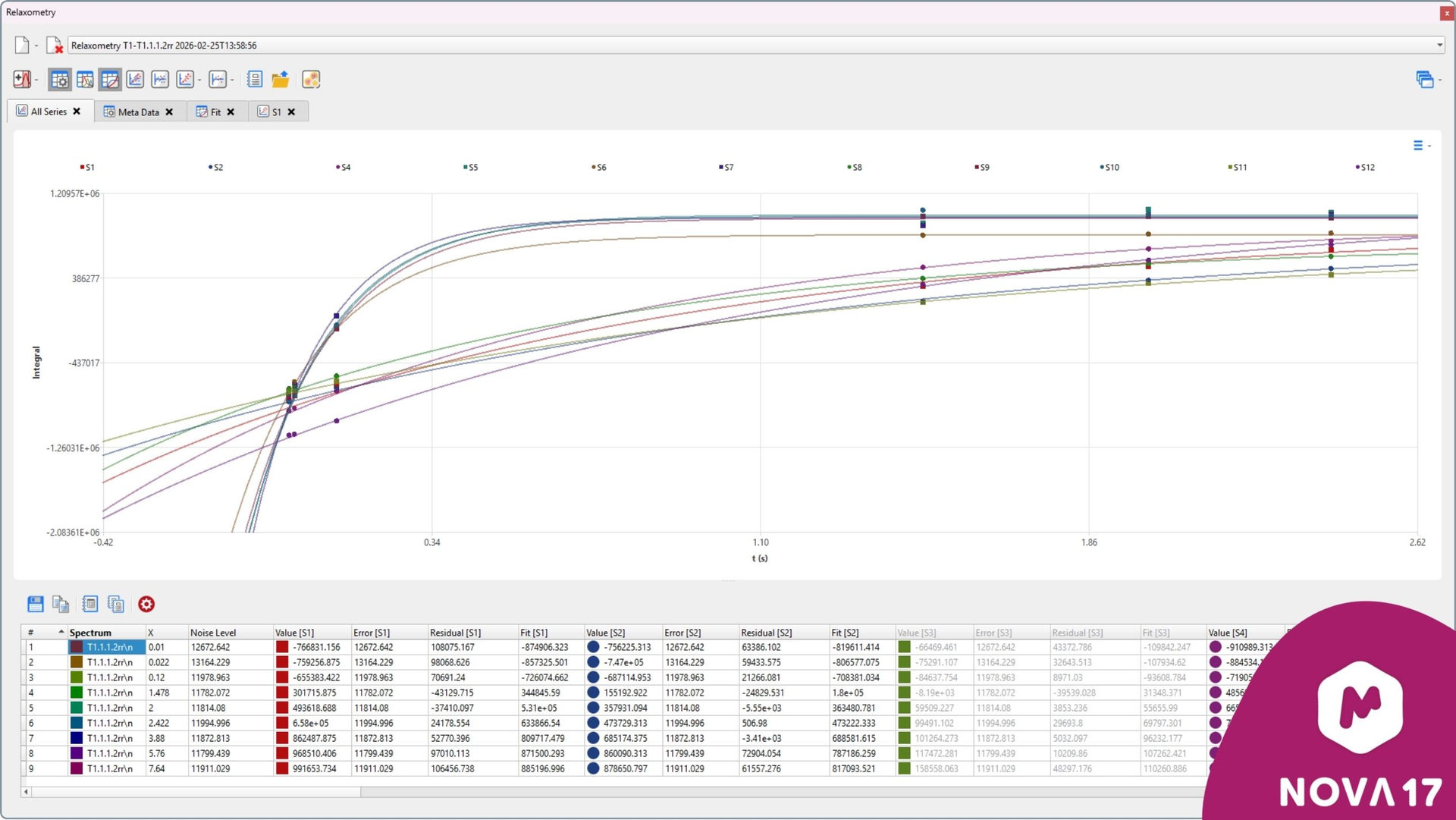
图 6:专用的Dynamics工作区,用于对底层行为进行更深入的分析和探索。
此修订版还引入了以下改进:
能够选择拟合模型中的成分数。
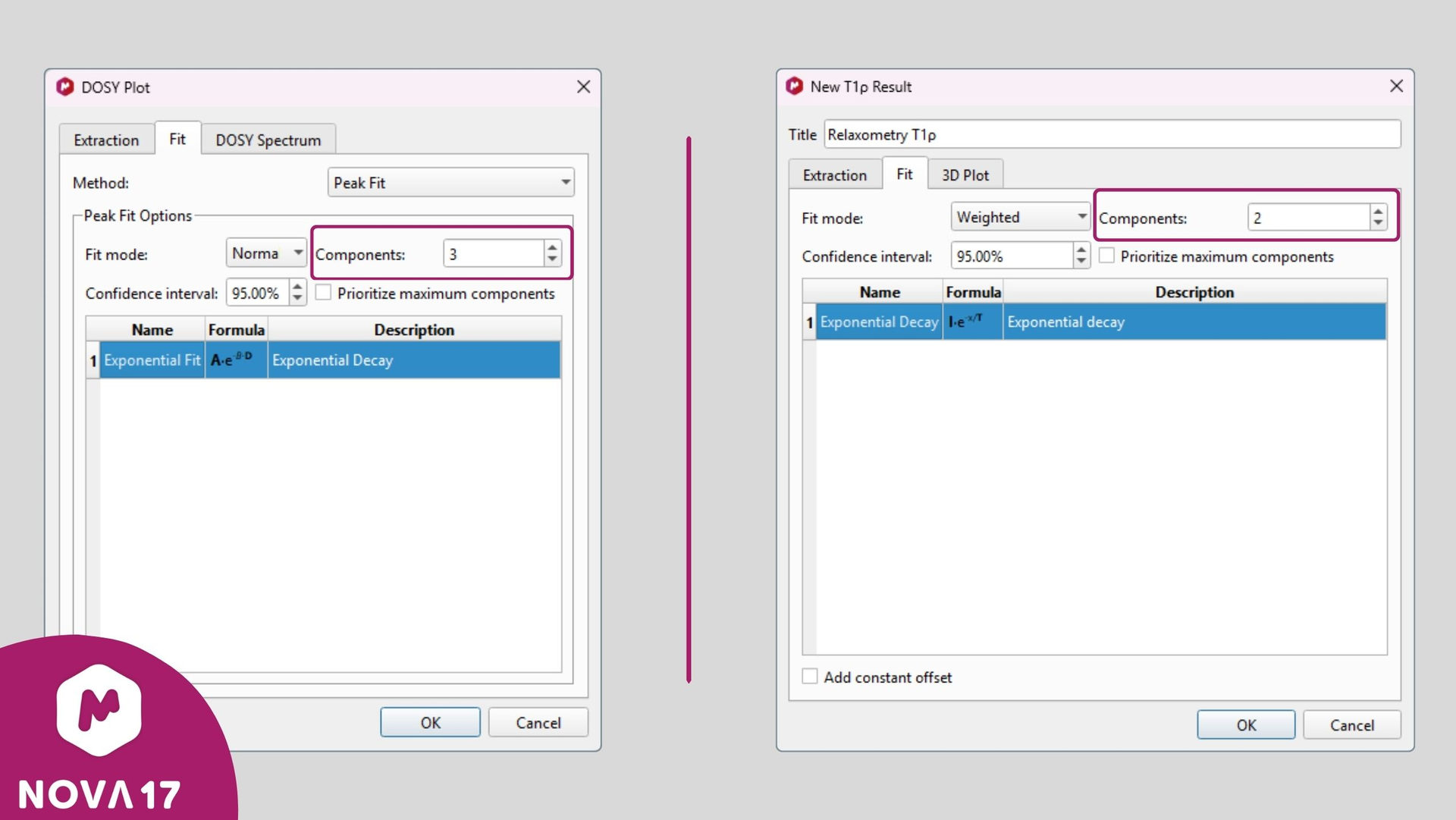
图 7:DOSY分析(左)和弛豫谱分析(右)中拟合成分数量的选择。
增强了图表和表格的交互性,包括:
- 绘制特定序列的个体残差。
- 在拟合过程中,排除噪声谱图中的损坏数据。
能够生成更全面的报告。
UniDec 算法:用于改善带电高分子量化合物的去卷积
由迈克尔·马蒂(Michael Marty)及其同事开发的 UniDec(通用去卷积)算法*, 旨在将复杂的质谱(MS)数据转换为易于解读的零电荷质量分布。通过采用强大的贝叶斯去卷积方法,UniDec能够实现精确的电荷态分配和波谱重建,即使在涉及电荷态重叠或未分辨同位素等棘手情况下亦是如此。
在Mnova 17中,用户现在可以在“电荷状态去卷积设置”窗口中,在久经考验的ZScore算法与业界公认的UniDec算法之间进行选择。这两种选项均可对m/z、电荷状态以及去卷积质量范围进行全面控制。这一增强功能为用户提供了一种前沿且被广泛采用的解决方案,能够以高速、高精度和高度可靠的方式分析15 kDa以上的生物分子。
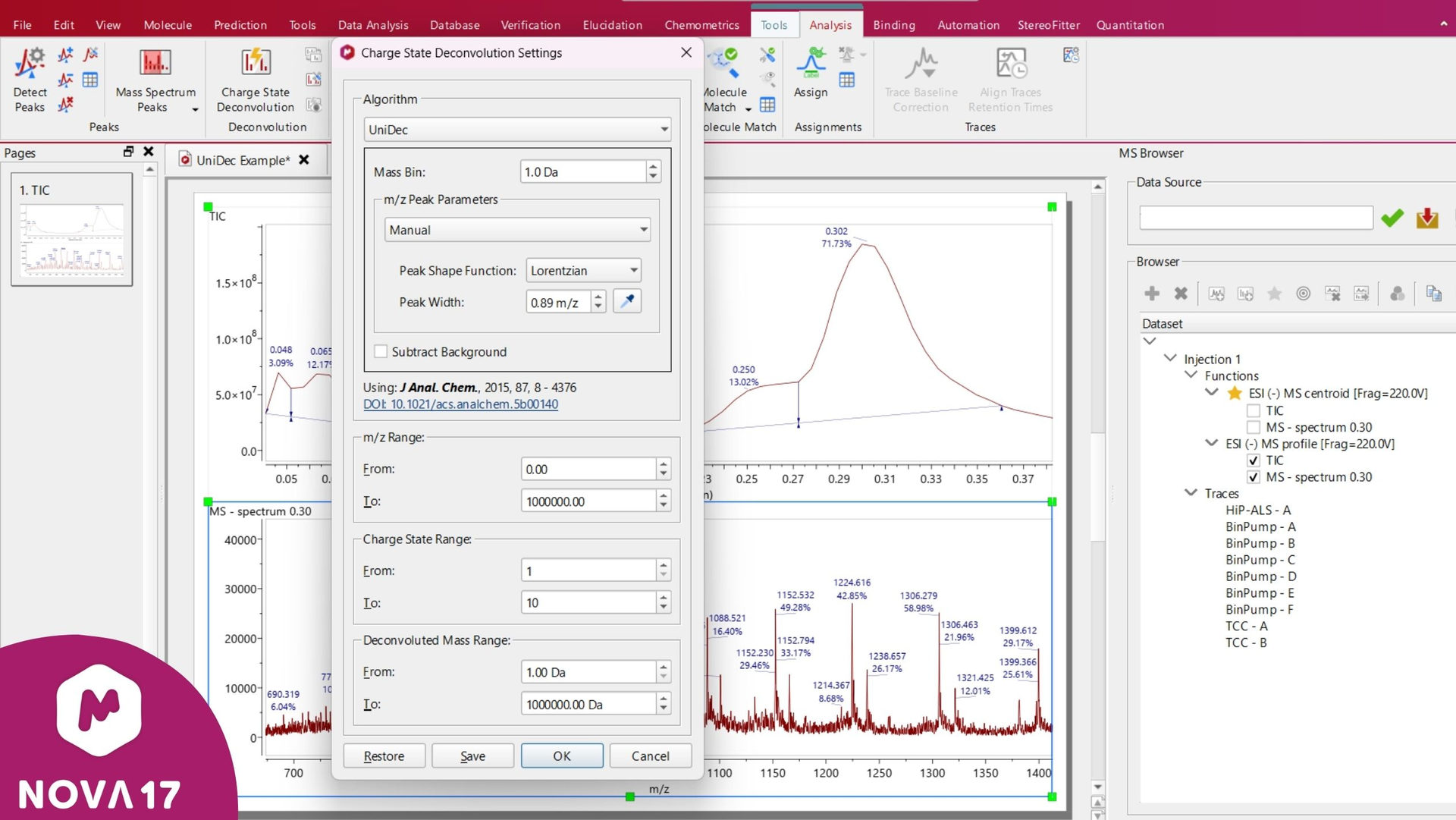
图 8:在“电荷状态反卷积设置”窗口中,用户可以在UniDec和ZScore算法之间进行选择,并为分析定义具体的阈值和范围。
*Anal. Chem. 2015, 87, 8, 4370–4376. https://doi.org/10.1021/acs.analchem.5b00140
电荷态谱图可视化
Mnova 17还引入了一项新功能,用于更好地在去卷积波谱中显示电荷态。当在“质谱峰”表中选中一个峰时,默认m/z波谱中会根据去卷积设置,将相应的电荷态位置高亮显示出来。
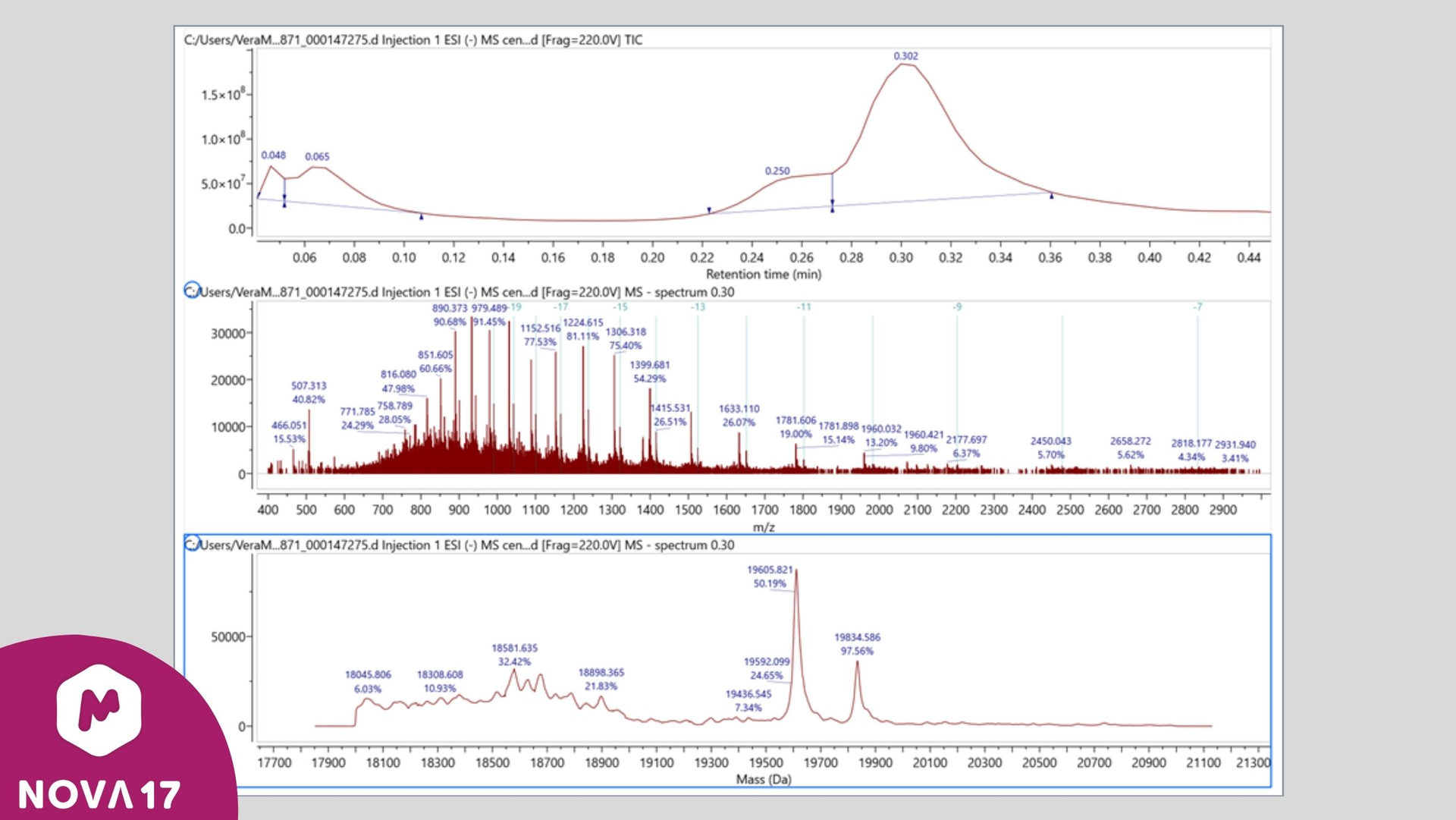
图 9:19 kDa分子量样本的UniDec去卷积结果示例。上图显示了总离子流色谱图,中图展示了去卷积波谱中的电荷态可视化结果,下图则呈现了去卷积后的波谱。
与岛津LC/GC-MS数据的兼容性
Mnova 17完全支持在Windows系统上处理岛津数据。此外,该软件现可获取岛津设备净化工作流程中生成的分馏信息,例如分馏的起止时间、管号及位置。
请查看MSChrom(LC/GC-MS)支持的文件格式以获取更多详细信息。
Mnova 17为Mnova DB和Mnova DB Server带来了多项令人兴奋的新功能:
用户现在可以通过添加、修改或删除项目和字段来编辑现有数据库,从而获得更大的灵活性和控制权。
现已新增对Microsoft SQL Server的支持,使Mnova DB Server能够在此广泛使用的后端上无缝运行。
现在可以运行直接与DB插件交互的Python脚本。这使用户能够编写自定义的Python程序来保存、更新或删除数据库元素,以及执行波谱和分子搜索——从而有效地扩展了Mnova DB中已有的所有操作。
此外,Mnova 17在后台实现了显著的性能提升,使Mnova DB比以往任何时候都更快、更高效。
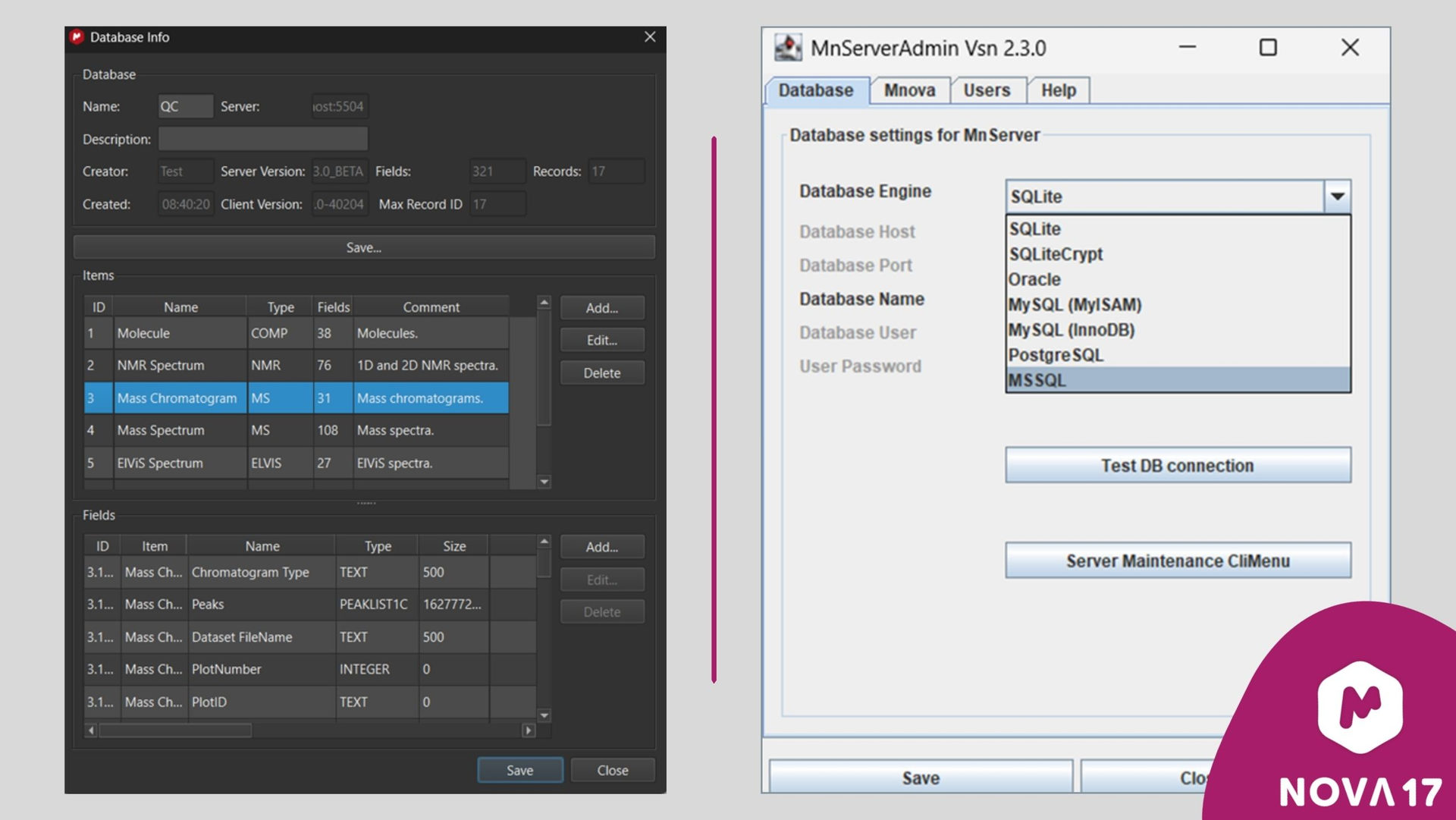
图 10:在Mnova的“数据库 > 管理 > 数据库信息”菜单路径下,用户现在可以通过添加、编辑或删除项目和字段来修改现有数据库的结构(左图)。在Mnova DB Server的设置菜单中,现在可以选择Microsoft SQL Server作为数据库引擎(右图)。
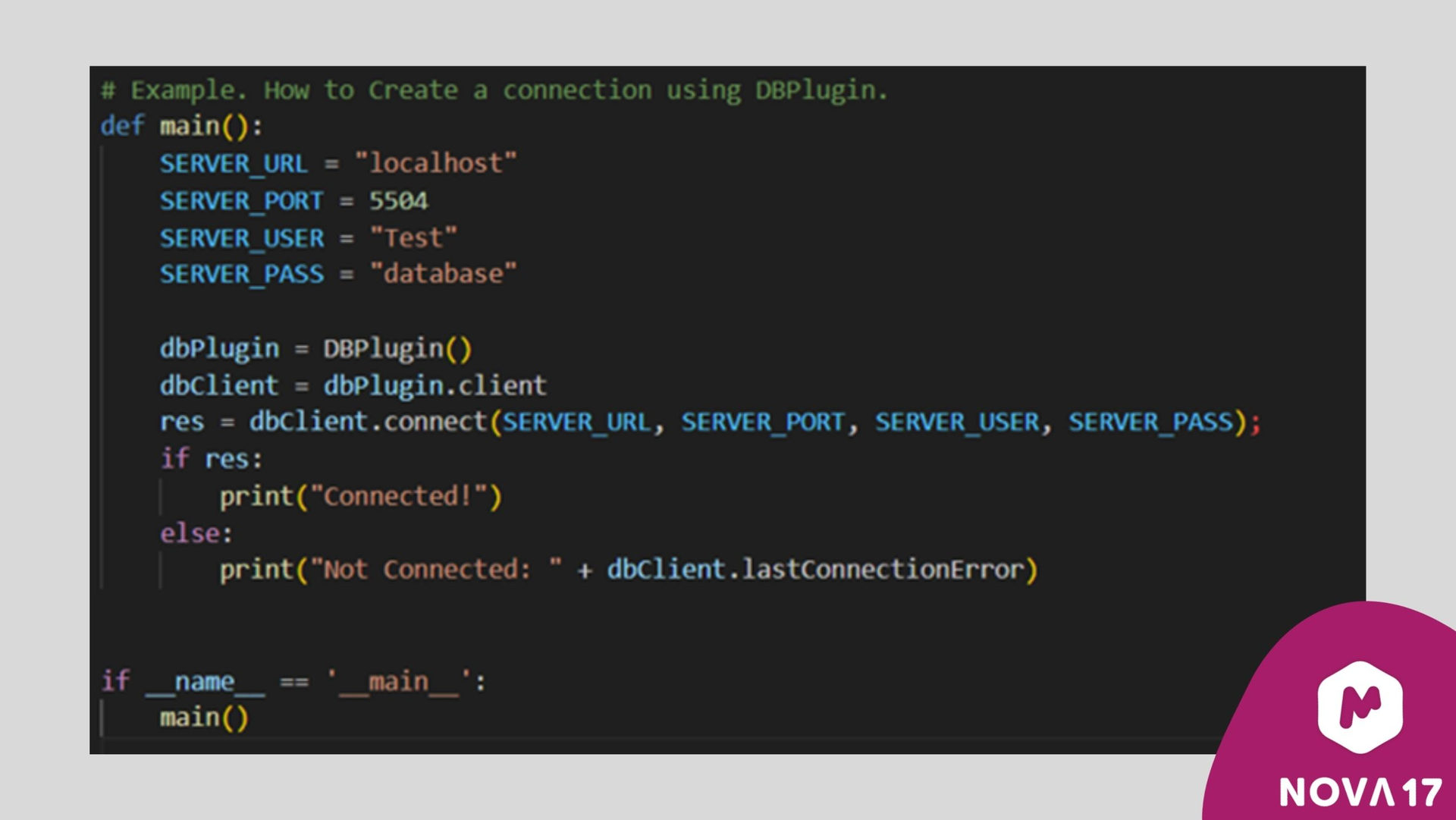
图 11:通过Mnova Python解释器与Mnova DB进行交互的Python脚本示例。
Mnova Gears 2.8.0带来了更流畅、更直观且更强大的分析体验。凭借增强的可视化功能、更智能的数据处理以及全新的效率提升功能,该版本让用户能够更快、更从容地开展工作。
Chrom Cal
借助Chrom Cal 1.2.0,用户现在可以为定量色谱图选择特定的进样口和功能,从而实现更精确、更精准的分析。此外,Chrom Cal经过优化,性能更佳,整体处理可靠性也更高。
Chrom RO、Fraction Analysis
通过各项改进和性能优化,Chrom RO 2.0.1和Fraction analysis 1.0.1能为您带来更流畅、更可靠的体验。
